Las roturas de la doble hélice de ADN parecen ser los primeros eventos carcinogénicos en pacientes con tumor papilar tiroideo, expuestos a las radiaciones durante el accidente nuclear de Chernóbil. Otros efectos, en el transcriptoma y el epigenoma, son descritos en Morton LM, Karyadi DM, Stewart C, Bogdanova TI, Dawson ET, Steinberg MK, et al. Radiation-related genomic profile of papillary thyroid cancer after the Chernobyl accident. Science 2021:eabg2538.
Un atlas con los perfiles de expresión génica, a partir de la secuenciación del ARN, describe 58 poblaciones celulares del pulmón humano, incluidas 14 desconocidas hasta ahora. Ello mejorará el estudio de las enfermedades respiratorias, entre otros impactos, según Travaglini KJ, Nabhan AN, Penland L, Sinha R, Gillich A, Sit RV, et al. A molecular cell atlas of the human lung from single-cell RNA sequencing. Nature 2020;587:619–625.
Filed under Diagnóstico, Transcriptómica by on . Comment. ![]()
 La inhibición de una precoz expresión génica y la señalización inflamatoria descontrolada, entre otras, son características que se relacionan con un riesgo mayor de muerte por ébola, revelados por perfiles transcriptómicos en ratones. Tal es el reporte en Price A, Okumura A, Haddock E, Feldmann F, Meade-White K, Sharma P, et al. Transcriptional Correlates of Tolerance and Lethality in Mice Predict Ebola Virus Disease Patient Outcomes. Cell Reports 2020;30(6):1702-1713.e6.
La inhibición de una precoz expresión génica y la señalización inflamatoria descontrolada, entre otras, son características que se relacionan con un riesgo mayor de muerte por ébola, revelados por perfiles transcriptómicos en ratones. Tal es el reporte en Price A, Okumura A, Haddock E, Feldmann F, Meade-White K, Sharma P, et al. Transcriptional Correlates of Tolerance and Lethality in Mice Predict Ebola Virus Disease Patient Outcomes. Cell Reports 2020;30(6):1702-1713.e6.
Filed under Patógenos, Polimorfismos, Transcriptómica by on . Comment. ![]()
 Con el uso de CRISPR-Cas9, la edición múltiple del genoma de linfocitos T produjo células con una mayor capacidad antitumoral, que se mantuvieron viables al menos por 9 meses. La nueva evidencia de las posibilidades de esta opción terapéutica es descrita en Stadtmauer EA, Fraietta JA, Davis MM, Cohen AD, Weber KL, Lancaster E, et al. CRISPR-engineered T cells in patients with refractory cancer. Science 2020:eaba7365.
Con el uso de CRISPR-Cas9, la edición múltiple del genoma de linfocitos T produjo células con una mayor capacidad antitumoral, que se mantuvieron viables al menos por 9 meses. La nueva evidencia de las posibilidades de esta opción terapéutica es descrita en Stadtmauer EA, Fraietta JA, Davis MM, Cohen AD, Weber KL, Lancaster E, et al. CRISPR-engineered T cells in patients with refractory cancer. Science 2020:eaba7365.
Filed under Cáncer, Medicina personalizada, Transcriptómica by on . Comment. ![]()
 La edición del ARN, que permitiría modificar las proteínas, podría ser más segura para generar terapias para las enfermedades genéticas, el cáncer, el dolor o la hipercolesterolemia. Lea un reciente comentario al respecto en Reardon S. Step aside CRISPR, RNA editing is taking off. Nature 2020;578:24-27.
La edición del ARN, que permitiría modificar las proteínas, podría ser más segura para generar terapias para las enfermedades genéticas, el cáncer, el dolor o la hipercolesterolemia. Lea un reciente comentario al respecto en Reardon S. Step aside CRISPR, RNA editing is taking off. Nature 2020;578:24-27.
Filed under Cáncer, Edición del genoma, Transcriptómica by on . Comment. ![]()
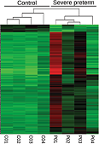 El análisis transcriptómico de las membranas amnióticas de niños a término o pretérmino permitió identificar la expresión diferenciada de genes de vías inflamatorias, inmunitarias, del sistema nervioso y la morfogénesis, que pueden ser candidatos a marcadores del parto pretérmino. Los detalles, en Pereyra S, Sosa C, Bertoni B, Sapiro R. Transcriptomic analysis of fetal membranes reveals pathways involved in preterm birth. BMC Medical Genomics 2019;12:53.
El análisis transcriptómico de las membranas amnióticas de niños a término o pretérmino permitió identificar la expresión diferenciada de genes de vías inflamatorias, inmunitarias, del sistema nervioso y la morfogénesis, que pueden ser candidatos a marcadores del parto pretérmino. Los detalles, en Pereyra S, Sosa C, Bertoni B, Sapiro R. Transcriptomic analysis of fetal membranes reveals pathways involved in preterm birth. BMC Medical Genomics 2019;12:53.
Filed under Diagnóstico, Transcriptómica by on . Comment. ![]()
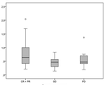 Los niveles de expresión de los miR-17-5p, miR-20a-5p, miR-30a-5p, miR-92a-3p, miR-92b-3p y miR-98-5p permiten predecir la respuesta al tratamiento en pacientes con cáncer colorrectal metastásico, si se combinan con aspectos clínicos como la edad, la diferenciación tumoral, la terapia adyuvante y el tipo de tratamiento sistémico. El hallazgo aparece en Neerincx M, Poel D, Sie DLS, van Grieken NCT, Shankaraiah RC, van der Wolf – de Lijster FSW, et al. Combination of a six microRNA expression profile with four clinicopathological factors for response prediction of systemic treatment in patients with advanced colorectal cancer. PLoS ONE 2018;13(8):e0201809.
Los niveles de expresión de los miR-17-5p, miR-20a-5p, miR-30a-5p, miR-92a-3p, miR-92b-3p y miR-98-5p permiten predecir la respuesta al tratamiento en pacientes con cáncer colorrectal metastásico, si se combinan con aspectos clínicos como la edad, la diferenciación tumoral, la terapia adyuvante y el tipo de tratamiento sistémico. El hallazgo aparece en Neerincx M, Poel D, Sie DLS, van Grieken NCT, Shankaraiah RC, van der Wolf – de Lijster FSW, et al. Combination of a six microRNA expression profile with four clinicopathological factors for response prediction of systemic treatment in patients with advanced colorectal cancer. PLoS ONE 2018;13(8):e0201809.
Filed under Cáncer, Transcriptómica, Tratamientos by on . Comment. ![]()
 Un método para el estudio de moléculas de ARN extracelular en los fluidos corporales ha permitido una caracterización preliminar que propone el potencial de estas moléculas como biomarcadores, que no son afectadas por el ayuno ni los ciclos hormonales. Así se comenta en Max K, Bertram K, Akat KM, Bogardus KA, Li J, Morozov P, et al. Human plasma and serum extracellular small RNA reference profiles and their clinical utility. PNAS June 5, 2018;115(23):E5334-E5343.
Un método para el estudio de moléculas de ARN extracelular en los fluidos corporales ha permitido una caracterización preliminar que propone el potencial de estas moléculas como biomarcadores, que no son afectadas por el ayuno ni los ciclos hormonales. Así se comenta en Max K, Bertram K, Akat KM, Bogardus KA, Li J, Morozov P, et al. Human plasma and serum extracellular small RNA reference profiles and their clinical utility. PNAS June 5, 2018;115(23):E5334-E5343.
Filed under Diagnóstico, Transcriptómica by on . Comment. ![]()
Filed under Bases de datos, Bioinformática, Cáncer, Medicina personalizada, Proteómica, Transcriptómica by on . Comment. ![]()
 Con la utilización de microarreglos en pacientes con osteoartritis avanzada que requerían reemplazo total de rodilla, se encontró la expresión aumentada de 218 genes, entre ellos stathmin 2, thrombospondin 4 y matrix metalloproteinase 13. La activación de moléculas de señalización Wnt/Notch/catenina/quimiocina puede explicar la habitual presencia de dolor en estos enfermos, de acuerdo con Kuttapitiya A, Assi L, Laing K, Hing C, Mitchell P, Whitley G, et al. Microarray analysis of bone marrow lesions in osteoarthritis demonstrates upregulation of genes implicated in osteochondral turnover, neurogenesis and inflammation. Annals of the Rheumatic Diseases 2017; doi: 10.1136/annrheumdis-2017-211396.
Con la utilización de microarreglos en pacientes con osteoartritis avanzada que requerían reemplazo total de rodilla, se encontró la expresión aumentada de 218 genes, entre ellos stathmin 2, thrombospondin 4 y matrix metalloproteinase 13. La activación de moléculas de señalización Wnt/Notch/catenina/quimiocina puede explicar la habitual presencia de dolor en estos enfermos, de acuerdo con Kuttapitiya A, Assi L, Laing K, Hing C, Mitchell P, Whitley G, et al. Microarray analysis of bone marrow lesions in osteoarthritis demonstrates upregulation of genes implicated in osteochondral turnover, neurogenesis and inflammation. Annals of the Rheumatic Diseases 2017; doi: 10.1136/annrheumdis-2017-211396.
Filed under Diagnóstico, Polimorfismos, Transcriptómica by on . Comment. ![]()



