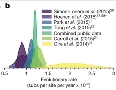
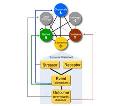
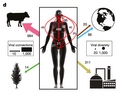
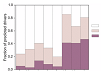
 Los métodos computacionales para la predición de genes relacionados con la aparición del cáncer varían significativamente en sus resultados, por lo que aún existen posibilidades de mejora para tales herramientas. Así se concluye en Tokheim CJ, Papadopoulos N, Kinzler KW, Vogelstein B, Karchin R. Evaluating the evaluation of cancer driver genes. PNAS 2016; doi: 10.1073/pnas.1616440113.
Los métodos computacionales para la predición de genes relacionados con la aparición del cáncer varían significativamente en sus resultados, por lo que aún existen posibilidades de mejora para tales herramientas. Así se concluye en Tokheim CJ, Papadopoulos N, Kinzler KW, Vogelstein B, Karchin R. Evaluating the evaluation of cancer driver genes. PNAS 2016; doi: 10.1073/pnas.1616440113.
Filed under Algoritmos, Bioinformática, Calidad, Cáncer by on . Comment. ![]()